高中生物学PCR技术中的引物设计
作者: 陈铁鑫
[摘 要]聚合酶链式反应(PCR)是江苏高考生物试题中的常考内容,PCR技术的用途并不局限于最初、最基本的获取目的基因。PCR技术的使用场景极其灵活,通过引物设计,可以达到融合基因、定点诱变等效果。文章对PCR技术中的引物设计思路进行分类,介绍其衍生的各种应用,为教师教学提供参考。
[关键词]PCR;引物设计;高中生物学
[中图分类号] G633.91 [文献标识码] A [文章编号] 1674-6058(2024)14-0084-04
核心素养是高考命题和各类考试命题的指导方向和原则。为加深学生对基因工程大概念的理解,提升学生的生物学科核心素养,《普通高中生物学课程标准(2017年版2020年修订)》要求教师在基因工程的教学过程中开展“利用聚合酶链式反应(PCR)扩增DNA片段并完成电泳鉴定,或运用软件进行虚拟PCR实验”活动[1]。引物直接决定PCR的特异性与成功与否。人教版高中生物学选择性必修三中通过图片简单演示了PCR的基本过程,并未涉及引物设计,而近几年各地的高考试题为了响应新课标要求,基于核酸检测、DNA测序等真实情境,增加了许多与引物设计相关的技术困境内容。为跨越教材与实际应用的鸿沟,笔者对不同应用场景中的引物设计进行分析,以促进学生对PCR的理解,为教师教学提供参考。
一、以基因定位为目的的反向引物设计
以真核生物为受体细胞时,目的基因一般需整合至受体细胞的染色体DNA中,以实现稳定存在与表达。在上述情境中,为进行目的基因定位,需要在已知目的基因的附近逐步搜索并测序相邻的DNA区域,这就需要用到反向PCR。
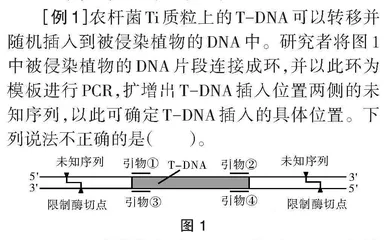
[例1]农杆菌Ti质粒上的T-DNA可以转移并随机插入到被侵染植物的DNA中。研究者将图1中被侵染植物的DNA片段连接成环,并以此环为模板进行PCR,扩增出T-DNA插入位置两侧的未知序列,以此可确定T-DNA插入的具体位置。下列说法不正确的是( )。
图 1
A.PCR扩增依据的是DNA分子双链复制的原理
B.进行PCR扩增需要热稳定DNA聚合酶
C.利用图中的引物②、③组合可扩增出两侧的未知序列
D.通过与受体细胞的基因组序列比对,可确定T-DNA的插入位置
解析:对含目的基因的T-DNA中两侧未知序列通过同种限制酶或是同尾酶进行酶切(目的基因中不能存在该酶的酶切位点),可取得相同的黏性末端。通过DNA连接酶令图 1含T-DNA的片段自身环化[2]成图2甲的环形DNA分子。
碍于DNA聚合酶的特性,子链总是从5'端往3'端延伸。若目的为扩增T-DNA,应选择指向已知扩增片段的内侧的引物②、③。选择引物①、④,子链向外侧未知序列进行延伸。由于PCR体系中没有DNA连接酶,因此子代DNA仍是线性(如图2乙)。扩增后,原本在两侧的未知序列被转移到已知序列的内部(如图2丙)。随后,我们可以对未知序列进行测序,比对受体细胞的基因组文库,即可确定T-DNA插入的位置。
图 2
参考答案:C
二、鉴定目的基因连接方式的反向引物设计
构建基因表达载体时,若使用单酶切可能出现目的基因的反向连接。目的基因的筛选与检测是基因工程的重要环节,可以通过设计引物进行PCR,筛选目的基因与载体的正向连接产物。
[例2]为鉴定筛选出的菌落中是否含有正确插入目的基因的重组质粒,拟设计引物进行PCR鉴定。图3所示为甲、乙、丙3条引物在正确重组质粒中的相应位置。
(1)PCR鉴定时应选择的一对引物是 。
(2)某学生尝试用图中另外一对引物从某一菌落的质粒中扩增出了400 bp片段,原因是 。
解析:如图 4所示,黑色区域为目的基因,我们在目的基因内、外各设计一引物,图中为正向连接时各引物序列的位置。使用引物1、引物3可扩增出对应片段,当目的基因反向连接时,引物1与引物3方向相同,无法有效扩增。同理,选择引物2、引物4,也可以进行上述验证。与预期相符的DNA长度就可以用于确认目的基因的正向连接。
图3为正向连接时的引物分布。引物丙、引物甲位于目的基因的上游和下游,无论连接方向是否正确,均可扩增出片段且长度相同,无法作为排除的依据。
若使用引物丙、引物乙进行PCR,考虑反向连接时,引物乙的方向与引物丙相同,无法扩增片段,正向连接时引物丙、引物乙可以扩增出350 bp长度的片段。
同理,若选择引物甲、引物乙进行PCR,反向连接时能扩增出400 bp片段,正向连接时无扩增产物,但空质粒也会带来相同的结果,无法确定实现了正向连接。
因此,PCR鉴定时应选择引物乙、引物丙。学生扩增出400 bp片段的原因是目的基因反向连接。
参考答案:(1)乙、丙 (2)目的基因反向连接
三、PCR体系中的引物序列改造
目的基因想要导入表达载体,两侧需要有合适的酶切位点。实验室用到的限制酶价格高昂,种类有限,为了不被基因自身序列限制,就需要对引物序列进行改造。引物设计的依据是目的基因的两侧序列,但这并不意味着引物需要与模板完全互补。我们既可以在5'端进行添加限制酶识别序列,也可以在中间进行少量碱基的增删或者替换。引物改造的部分序列不能和原对应模板配对,但不影响引物和模板的整体配对,因此,其扩增产物的对应位置就会引入识别序列,或是发生碱基对的增删或者替换[3]。
(一)引入序列与连接DNA
引物与模板的结合并不需要完全一一对应。引物的3'端是DNA聚合酶添加游离脱氧核苷酸的位点,如果引入的核苷酸序列添加在3'端,会导致扩增产物的特异性下降。因此,我们常常只在5'端添加所需要的酶切位点。若在两个DNA片段对应引物的5'端分别构建相同或者互补序列,对获得的新DNA进行变性与杂交,还可以达到连接DNA的效果。
[例3]科研人员通过敲除里氏木霉基因组中去乙酰化酶基因(HDAC),探究组蛋白乙酰化对纤维素酶基因表达的影响,其主要过程如图5。请据图回答:引物设计是PCR的关键,本研究中引物R1的5'端添加与引物FG互补的序列,其目的是 。在PCR5中加入的引物是 。
图 5
解析:通过PCR1、PCR2,可获得新霉素抗性基因GR与H1的构造(如图 6)。
图 6
以GR 基因、H1为模板,F1和RG为引物进行PCR4扩增,在高温作用下双链会打开。由题可知,引物R1的5'端添加了与引物FG互补的序列,因此其延伸产物H1基因的b链5'端也存在引物FG的互补序列,b链与c链就能够部分配对(如图 7)。Taq DNA聚合酶只能从5'端向3'端延伸,这两条链的3'端都缺乏模板,无法继续延伸。
图 7
a链的3'端与R1序列互补,d链的3'端与FG互补。由于R1与FG互补,因此a链的3'端和d链的3'端也是互补的(如图 8)。
图 8
在Taq DNA聚合酶的作用下,可将重叠的两条链补齐(如图9)。
图 9
两个基因就这样融合成功。随后a链、d链分别结合引物RG、F1进行PCR4,就得到了大量的H1-GR融合基因。这种借助引入序列连接DNA的方法我们称为重叠延伸PCR。按照相同的逻辑,可以将基因H2和GR也进行连接。
图10
如图10,通过类比,不难想到应令c链和f链发生互补配对、延伸。随后c链、f链分别以R2、FG为对应引物,进行大量扩增。为确保这两条链的碱基互补配对,可在F2的5'端通过引入序列,添加与RG互补的序列。
综上,本研究中在引物R1的5'端添加与引物FG互补的序列,其目的是便于PCR4时H1和GR基因的连接。在PCR5中加入的引物是R2和FG。
参考答案:便于H1和GR的拼接 R2和FG
(二)定点诱变
引物是PCR产物5'端的一部分,引物长度一般为15~27 bp,因此最初建立的PCR定点诱变技术只适用于DNA的末端突变。突变位点在基因中部时,我们就得设计两对引物,基因中部的两个诱变引物分别与两侧常规引物将目的基因分段扩增,再以上文中连接DNA的方式将两段诱变DNA融合。
[例4]重叠延伸PCR技术是采用具有互补末端的引物,使PCR产物形成重叠链,从而在随后的扩增反应中通过重叠链的延伸,获得想要的目的基因。某科研团队运用重叠延伸PCR技术在水蛭素基因的特定位点引入特定突变,以实现基因的定点突变,原理如图11。下列说法错误的是( )。
图11
A. 过程②需要含Mg2+的缓冲液、DNA模板、引物、四种脱氧核苷酸、耐高温的DNA聚合酶等
B. 若引物1、引物2组成的反应系统和引物3、引物4组成的反应系统中均进行一次DNA分子的复制后,一共会产生3种DNA分子
C. 经过过程④获得的杂交DNA有2种,其中只有一种可以经过过程⑤获得目的基因
D. 过程⑤使用耐高温的DNA聚合酶延伸,需要引物
解析:过程④获得的杂交DNA具有游离的3'端,也具有模板,可以直接使用耐高温的DNA聚合酶延伸,不需要引物。其连接机制与例3相同。